使用SimBiology Model Builder将SGLT2抑制纳入基于生理的葡萄糖-胰岛素模型
本例展示了如何通过假设化合物将SGLT2抑制添加到现有的葡萄糖-胰岛素模型SimBiology模型构建器.
Glucose-Insulin模型
该模型是本文中引用的葡萄糖-胰岛素模型的另一个SimBiology实现模拟葡萄糖-胰岛素反应的例子。该模型基于Dalla Man等人的出版物。在他们2007年的出版物中[1],作者开发了一个人餐后葡萄糖-胰岛素反应的模型。该模型用常微分方程描述了系统的动力学。作者使用他们的模型来模拟一顿或多顿饭后的葡萄糖-胰岛素反应,包括正常的人类受试者和各种胰岛素损伤的人类受试者。
钠-葡萄糖共转运体-2 (SGLT2)抑制
SGLT2受体已被证明可促进约50%的肾脏葡萄糖再吸收[3].本例假设有一个假设的SGLT2抑制剂化合物,抑制SGLT2 50%。还假定了合理的给药方案和药代动力学特性。在本例中,将该抑制剂化合物的药代动力学/药效学(PK/PD)纳入葡萄糖-胰岛素模型。
通过添加和配置反应合并抑制剂PK
在接下来的步骤中,通过使用两个反应模拟假设的SGLT2抑制剂化合物的化合物吸收和清除。
负荷模型
打开SimBiology模型构建器点击应用程序SimBiology模型构建器在应用程序TAB或键入
simBiologyModelBuilder在命令行。在首页应用程序的标签,选择开放.
导航到文件夹
matlabroot\ \ simbio \ \数据示例.matlabroot是安装MATLAB的文件夹。进入matlabroot在命令行中提供根文件夹的路径。选择命名为SGLT2_model_incomplete.sbproj.点击开放.
添加和配置反应
请注意
在macOS上,使用命令键而不是Ctrl.
的工具栏中拖放两个物种块图选项卡。您可以将它们放在注释块的下面治疗,这只是一个标签(文本)块。

新闻Ctrl从第一个物种拖一条线到第二个物种。一个反应块出现在中间。这个反应代表了化合物的吸收。
通过双击编辑默认物种名称。重命名
species_1来GI_SGLT2_Inhib而且species_2来Plasma_SGLT2_Inhib.
点击反应块。在属性编辑器右边的窗格,改变反应的名字来
compound_absorption.在动态法部分,更改自动创建的向前速度参数kf来
k_compound_absorption.该模型已经具有正向速率参数k_compound_absorption这是之前创建的。该应用程序在反应速率表达式中使用绿色文本作为参数名称,蓝色文本用于物种名称。提示
如需更改默认反应配置,请单击首选项在首页选项卡。在首选项对话框中,单击模型建立.在反应建筑节中,有三个选项可以更改默认的动力学定律,为动力学定律创建参数,以及更改所创建参数的范围。
在州表中,将两个物种的单位设置为
毫克.
从图表工具栏中拖放另一个反应块以模拟复合间隙。
新闻Ctrl拖一条线
Plasma_SGLT2_Inhib反应。
提示
如果这些块没有对齐,您可以使用对齐工具对齐它们。在首页选项卡上,选择图工具>
图表对齐工具.点击反应块。在属性编辑器Pane,改变反应的名字来
compound_clearance.更新反应速率来
CL / Vd * Plasma_SGLT2_Inhib.CL而且Vd分别给出模型中间隙和容积的分布参数。
提示
新加入的反应的动力学定律被设定为MassAction默认情况下,SimBiology模型构建器App自动创建和映射反应速率所需的物种和参数。对于其他的动力学定律,只有参数被创建和映射。您需要手动创建和映射物种。使用未知的动力学定律,定义自定义的反应速率与自己的参数。您必须定义并添加自定义速率所需的物种和参数。
的MassAction而且未知的即使反应速率相同,动力学规律也会有不同的模拟结果。当不同区域的物质发生可逆反应时就会发生这种情况。模拟结果的差异是由于SimBiology在量纲分析期间进行了体积缩放。详细信息请参见从反应中得到颂歌.具体地说,为MassAction, SimBiology使用相应的隔间体积来乘以正向和反向速率。然而,对于未知的和其他内置的动力学定律,SimBiology将整个速率仅乘以一个包含反应物的隔间。要确切地查看用于缩放的隔间体积,请打开方程选项卡,查看常微分方程部分。
利用数学方程合并抑制剂PD
SimBiology允许您定义一个数学表达式,以在模拟过程中定义或更新模型量的值。详细信息请参见SimBiology模型中规则的定义与评价.在接下来的步骤中,您可以添加一个重复分配规则,通过定义基于复合疗效的血浆葡萄糖排泄的肾脏阈值来纳入抑制剂的药效学。
在浏览器窗格中,单击浏览器工具栏上的加号图标并选择
增加重复分配.的最后一个空行重复作业表格
双击该行,输入基于Hill方程的复合抑制表达式:
renal_threshold = basal_renal_threshold*(1-compound_Imax* whole_body . plasma_sglt2_inhibitb ^2/(compound_IC50^2+ whole_body . plasma_sglt2_inhibitb ^2))
的图属性的重复分配规则块
renal_threshold参数。提示
要查看整个模型并对其进行平移,请展开模型评估工具在浏览器窗格,然后单击概述.

请注意
应用程序只显示重复赋值规则、速率规则或事件函数的左侧(LHS)的参数的参数块。
该应用程序只显示重复分配和费率规则的规则块。
该应用程序使用虚线来连接规则右侧的数量。默认情况下,不显示这些行。要显示行,单击规则块。从属性编辑器窗格,在块节中,设置表情纹来显示.
更新肾脏排泄反应纳入抑制剂化合物的存在
该模型的肾排泄反应目前定义为血浆葡萄糖->尿葡萄糖- excr_auc反应速率参数glucose_excretion.速率参数由重复赋值规则定义为葡萄糖排泄=(血浆葡萄糖>renal_threshold)*GFR*(血浆葡萄糖renal_threshold),在那里肾小球滤过率(GFR)为肾小球滤过率,决定反应通量,影响SGLT2抑制效果。
在以下步骤中,您更新肾脏排泄反应血浆葡萄糖+血浆sglt2_inhibitb ->血浆sglt2_inhibitb +尿葡萄糖excr_auc_24hr,其中抑制剂化合物Plasma_SGLT2_Inhib既是反应物又是反应的产物。
在图选项卡,单击灰色方形反应块命名
肾排泄.
在属性编辑器窗格中,更新反应字符串
血浆葡萄糖+血浆sglt2_inhibitb ->血浆sglt2_inhibitb +尿葡萄糖excr_auc_24hr.现在连接一条虚线Plasma_SGLT2_Inhib到反应区图选项卡。请注意
SimBiology使用虚线表示一个物种既是反应物又是反应的产物,并且没有被反应消耗。

分裂和克隆块
当有多个对相同数量的引用时,多行连接到块。为了使图表更清晰,您可以分割块,即创建同一块的副本,以便每个引用都连接到块的不同副本。您还可以克隆一个块来为它添加其他用途。例如,您可以首先克隆一个物种块以在多个表达式中引用。然后,您可以在构建模型时在每个表达式中使用每个克隆。
在以下步骤中,将克隆Plasma_SGLT2_Inhib块。这些步骤是可选的,对模型行为没有任何影响。
单击
Plasma_SGLT2_Inhib图中的块。在属性编辑器窗格,滚动到分裂部分。
点击克隆.

在图选项卡,克隆块将出现在原始块的旁边。现在每个块都有一个克隆指示器。

现在可以将虚线移动到克隆块。首先单击虚线。新闻Ctrl并将虚线拖到克隆块上。当该行靠近克隆块时,会出现一个绿色加号图标。释放鼠标以将该行附加到克隆块。

的位置移动克隆块
肾排泄反应块,使图表更容易阅读。
利用事件在模型行为中合并突然的变化
您可以基于指定的条件对模型行为中的突然变化进行建模。例如,您可以在某个时间点或超过某个浓度阈值时重置物种数量。SimBiology允许您使用称为事件的建模组件对此类更改建模。事件允许您指定在自定义条件为真时发生的数量值的离散转换。这样的条件称为事件触发器。一旦条件变为真,就执行一个或多个事件函数。详细信息请参见SimBiology模型中的事件.
在以下步骤中,通过添加一个事件触发器和五个事件函数,每24小时将尿葡萄糖总量重置为零。
单击浏览器工具栏上的加号图标。选择
添加事件.的最后一个空行事件表格
输入以下事件触发器:
time >= (num_day+1)*timeDay.在接下来EventFcn行,输入
尿葡萄糖excr_auc_24hr = 0.
若要向同一事件添加第二个事件函数,请转到属性编辑器事件的窗格。在事件Fcns表中,双击空行,输入如下内容:
Num_day = Num_day + 1.
新增三个事件函数,如下所示:
Plasma_Glucose_Conc_AUC_24hr = 0Vmax_dep_glucose_util = Vmax_dep_glucose_util_baselineBeta_glucose_signal = beta_glucose_signal_baseline
.

添加剂量
SimBiology允许您模拟由于刺激(如口服或静脉注射药物)引起的物种数量的增加。要模拟这种物种数量的增加,请使用剂量建模组件。在以下步骤中,模拟抑制剂药物的摄入量,例如每天一次x天数,通过给药GI_SGLT2_inhib物种。
在浏览器窗格,单击显示剂量工具栏上的图标。

的剂量选项卡出现了。在剂量节,每一行代表一个剂量。的类型列让您选择重复剂量(默认),计划剂量.的活跃的列允许您在模拟模型时选择要应用的剂量。
双击的名字列中最后一个空行,然后输入
SGLT2 Inhib QD.
在属性节,目标名称,输入
GI_SGLT2_Inhib并选择Whole_Body。GI_SGLT2_Inhib.在剂量节,输入以下内容:
量=
300率=
0开始时间=
timeBreakfast时间间隔=
1440RepeatCount=
7
在单位节,输入以下内容:
AmountUnits=
毫克RateUnits=
TimeUnits=
一分钟

使用变体表示生物变异性
你可以使用一个叫做a的建模组件对生物变异性进行建模变体.变量是具有可选值的数量的集合。例如,在本例中,您可以为2型糖尿病患者设置一组参数值,为非2型糖尿病患者设置另一组参数值。
为了本例的目的,模型已经有两个变体。在以下步骤中,您将打开变体选项卡,您可以在其中编辑或添加更多变体。
在浏览器窗格,单击显示变量工具栏上的图标。

的变体选项卡出现了。在变体节中,每一行表示一个变体。的活跃的列允许您选择在模拟模型时应用哪些变量。您可以选择多个变量,如果数量值有重复的规格,则在模拟过程中使用变量数组中最后出现的值。应用程序按照变量在表中从上到下出现的顺序应用变量。重新排序变量可以改变初始条件,因为变量是按新的顺序应用的。中模拟模型时,请确保提供正确的顺序模型分析应用程序。价值中的列。内容部分显示应用所选的所有变量后的最终数量值。

默认情况下,内容节只显示那些被变体修改的量。要查看所有型号数量,请选择
显示模型中的所有数量在显示部分。
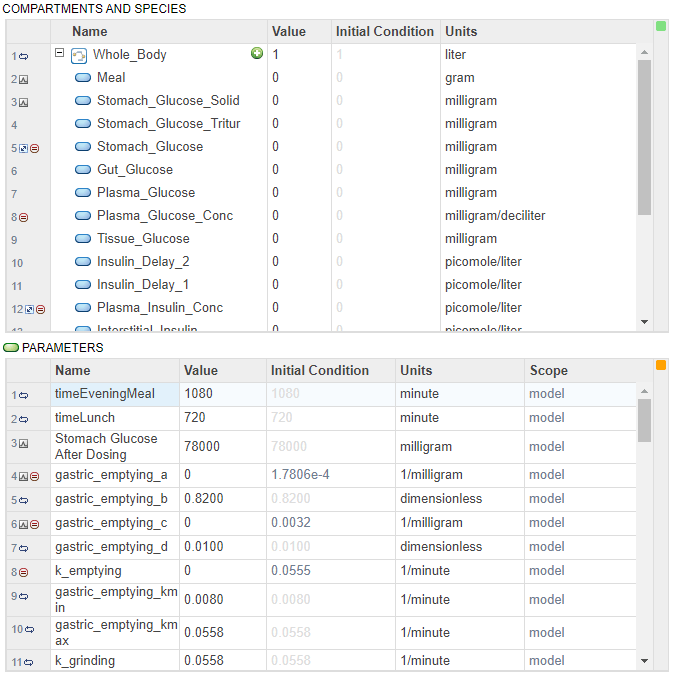
显示模型方程和初始条件
您可以查看基本的方程组,即常微分方程(ode)和表示模型的规则。SimBiology从模型反应中得到ode, ode定义了在模型模拟过程中积分的量。详细信息请参见模型仿真.
您可以使用模型方程和初始条件来调试模型。例如,您可以检查ode的初始条件,以查看数量值是否按预期进行了初始化。您还可以看到SimBiology如何通过用隔间体积分割方程的右边来纠正ode的尺寸。体积校正信息可以帮助您调试意外的模拟结果,特别是当您拥有具有不同体积的多室模型时。
要查看模型方程,请单击显示模型方程工具栏上的浏览器窗格。
![]()
应用程序打开方程选项卡。
反应的通量
默认情况下,该应用程序在模型方程中显示反应通量时嵌入反应通量。清除嵌入通量复选框以查看通量部分分开。

一般情况下,反应通量与反应速率相等,但通量的尺寸总是相等的/时间.反应速率的维度可以是浓度/时间或/时间.详细信息请参见从反应中得到颂歌.
初始条件
您可以查看模型数量的初始条件,即隔间、物种和参数。初始条件是模拟时间= 0时的数量值。工具栏上浏览器窗格中,选择查看模型文档选项>显示模型初始条件.

该应用程序添加了一个名为初始条件到隔间和物种表和参数表格
定义可观察表达式
SimBiology允许您通过定义和计算自定义表达式来执行后模拟计算。这样的表达式叫做an可观测的.在以下步骤中,您将可观察表达式添加到模型中,以计算血浆葡萄糖浓度-时间剖面的Cmax和平均值。
单击浏览器工具栏上的加号图标。选择
添加可观察到的.的最后一个空行可见表格
双击空行,输入以下表达式获取Cmax值:
Cmax_plasma_glucose = max(Plasma_Glucose_Conc).
进入单位可观察到的是
毫克/分升在属性编辑器.
双击下一个空行,输入以下表达式得到平均值:
Mean_plasma_glucose = mean(Plasma_Glucose_Conc).
进入单位可观察到的是
毫克/分升在属性编辑器.
使用模型仿真工具可视化模型行为
方法可以可视化模型动态模型仿真工具。该工具提供了一种方便的方法来模拟模型和绘制模型量或观测值的时间过程,而不必在模型中运行模拟程序模型分析应用程序。
的模型仿真工具位于应用程序的右侧属性编辑器窗格。在接下来的步骤中,绘制物种的时间进程Plasma_Glucose_Conc而且GI_SGLT2_Inhib.
请注意
如果您还没有完成前面的模型构建步骤,您可以加载已完成的项目来继续本教程。
打开SimBiology模型构建器应用程序。
点击开放并导航到该文件夹
matlabroot\ \ simbio \ \数据示例.matlabroot是安装MATLAB的文件夹。选择命名为SGLT2_model.sbproj.
工具的下方,单击工具名称旁边的箭头属性编辑器窗格。

点击添加图在工具栏上。
Plot1出现了。双击下面的单元格组件名称和类型:
Plasma_Glucose_Conc当你打字时,应用程序会提供建议。选择
Whole_Body。Plasma_Glucose_Conc.
选择选项>
为模拟定义活动变量.它打开变体选项卡。
选择2型糖尿病在变体表中。

选择选项>
为模拟定义有效剂量.它打开剂量选项卡。选择每天的早餐,每天的午餐,每天晚上,SGLT2 Inhib QD剂量表中。
点击运行在工具栏上查看物种的时间进程。

要导出图形,将鼠标指向表格的右上角,然后单击选项菜单图标。点击出口的阴谋从名单上。

您还可以使用模型数量的上下文菜单将它们添加到模拟工具中的现有图或新图中。去图TAB(或在浏览器窗格),右键单击GI_SGLT2_Inhib物种和选择情节状态>Plot1.该物种现在被添加到plot中。

点击运行再次更新剧情。

出口模式
SimBiology模型构建器允许您将模型导出为各种文件格式。您可以:
在首页选项卡,在模型部分中,选择出口.

提示
您可以在。中找到这个示例的完整模型matlabroot\ \ simbio \ data \ SGLT2_model.sbproj例子,在那里matlabroot是安装MATLAB的文件夹。
参考文献
[1]达拉·曼,基亚拉,罗伯特·a·里扎,克劳迪奥·科贝利。葡萄糖-胰岛素系统的膳食模拟模型IEEE生物医学工程汇刊54岁的没有。10(2007年10月):1740-49。https://ieeexplore.ieee.org/document/4303268.
[2]达拉·曼,基亚拉,卡米列里和c·科贝利。口服葡萄糖吸收的系统模型:金标准数据的验证。IEEE生物医学工程汇刊53岁的没有。12(2006年12月):2472-78。https://ieeexplore.ieee.org/document/4015600.
[3]赖特,欧内斯特M.,唐纳德D. F.卢,布鲁斯A.平山。《人体钠葡萄糖转运体生物学》生理上的评论91年,没有。2(2011年4月):733-94。https://journals.physiology.org/doi/full/10.1152/physrev.00055.2009.
另请参阅
SimBiology模型分析器|SimBiology模型构建器




























